|
|
但是,人類發明的任何體外擴增體系都是不完美的,無法做到100%精確拷貝最初的DNA樣本,每一次複製都會帶入一丁點錯誤。就像複印文稿總比原稿品質差一些一樣,經過千萬次複製再複製,就足以讓這份DNA樣本變得面目全非,干擾檢測結果。
多次下載圖片再重新上傳也會導致圖片文件出現明顯的「劣化」。
這一切引入的「噪音」甚至比脫靶信號本身還要高出好幾個數量級,這宛如是在汪洋大海中尋找一滴水一般。
一舉三得該如何實現?
找到這滴水的唯一辦法就是讓大海(各種干擾因素)消失。左二偉博士與導師楊輝還真的想到了一種絕妙的方式,同時解決了這三個問題。
為了避免個體差異,我們又需要找到兩個基因一模一樣的細胞,為了凸顯脫靶的信號,我們又需要用到「單細胞測序」,然後我們還不能用體外擴增來複制這兩個細胞的DNA,卻又需要很大量的DNA樣本來做測序分析。
首先最容易解決的就是找兩個基因完全一模一樣的細胞。我們知道,多數動物都是從一個受精卵發育而來的,這個受精卵一分為二,二分為四……等等,在它一分為二的時候,我們稱之為「二細胞期胚胎」階段,不就是兩個現成的基因一模一樣的細胞嗎?
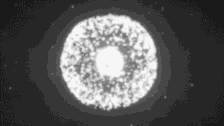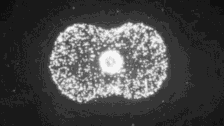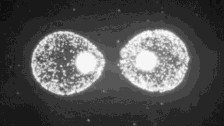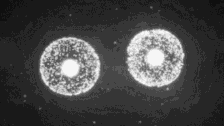
只要向其中一個注射基因編輯工具,另一個就是世界上最佳的對照。
其次,一個細胞的DNA不是不夠檢測么?沒關係,注射完畢后我們直接把這個二細胞胚胎植入母鼠的子宮當中,讓它正常發育,這樣得到的小鼠胚胎中,理論上就有一半細胞經歷過基因編輯,另一半則沒有經歷過過。
這時候,左二偉博士直接將發育長大的小鼠胚胎取出來,用一些特殊的酶消化成一大堆分散的細胞。利用一些方法,我們可以追蹤當時那兩個細胞的後代,從這一堆細胞中將它們倆各自的後代分成兩撥。由於這兩撥細胞也是之前的細胞分裂而來,所以它們的基因就相當於是最初那個細胞的複製品。
這也順便解決了第三個問題,裂解掉這一大堆足以構建出半個小鼠胚胎的巨量細胞,一次性就能提取到足夠測序分析的DNA,從而避免了體外擴增帶來的噪音。
在神經所蒲慕明所長的建議下,研究團隊將這套系統命名為GOTI。可以說,這套系統的推出,標誌著人們終於得以用數字來衡量基因編輯的脫靶率。
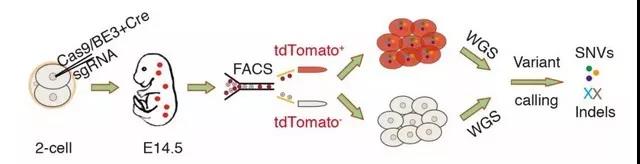
GOTI的技術流程:在二細胞期向一個卵裂球注射基因編輯工具,並用CRE使之本身以及後代細胞都發出紅色熒光。等小鼠胚胎髮育到14.5天後取出母體,利用流式細胞儀將兩個卵裂球的後代分開,並各自全部消化掉提取DNA來做測序分析。
哪種基因編輯易脫靶?我們挨個測一下
終於到了檢測工具一顯身手的時候。它接下來要幫助人們回答的關鍵問題就是:那些常見的基因編輯工具真的會脫靶嗎?在GOTI的神威下,一切清晰了起來。
首先,值得慶幸的是,最經典的spCas9系統經受住了考驗。結果顯示,它引起異常基因突變的可能性不高於小鼠自身細胞分裂帶來的本底基因突變。就是說,從目前的檢測結果來看它是安全的。
CRISPR-Cas9系統已經成為目前最方便的基因編輯工具。圖片來源:origene.com
與此同時最令人大跌眼鏡的發現是,另一類叫做單鹼基突變系統(Base Editor)的基因編輯工具有著異常高的脫靶率。所謂的單鹼基突變系統,大致上可以理解為我們先設計一個只能精確靶向但不會切割DNA的Cas9蛋白,然後讓這個Cas9蛋白牽著一個能夠通過化學方法將某個鹼基定向突變(比如A→T)的酶來給DNA鏈中引入點突變。
原本這套系統因為不會引入DNA斷裂,被視為特別安全的一類基因編輯技術,人們從來不覺得它會脫靶,之前的脫靶檢測也完全沒有發現它有任何脫靶的跡象。因此以劉如謙(David Liu)等為代表的一群科學家長期都在致力於將這項技術作為基因編輯向臨床進軍的急先鋒。
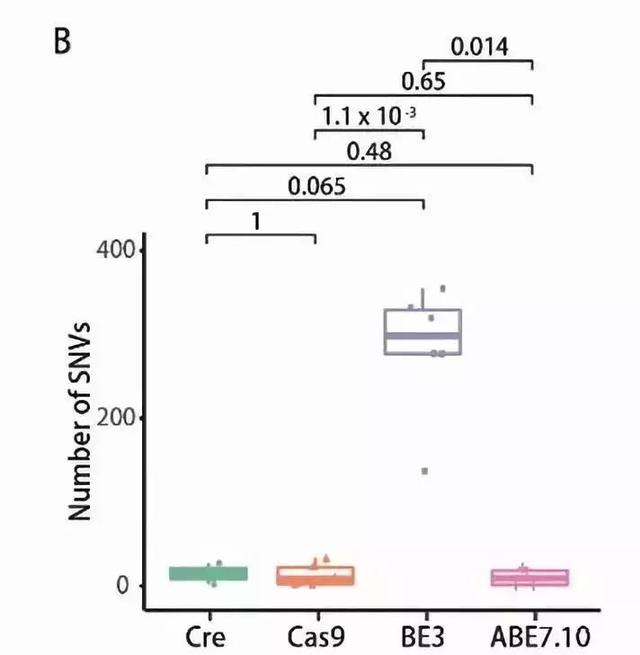
通過檢測發現,經典的CRISPR/Cas9並沒有顯著的脫靶現象,但是單鹼基編輯系統BE3則出現了高出背景基因突變水平數倍的脫靶現象。
這時候研究團隊才突然意識到,就算Cas9沒有在sgRNA帶領下跟任何DNA序列結合,那個能夠引起鹼基定向改變的酶也依舊存在,它完全可以像任何在細胞里遊離的酶一樣,讓任何偶然接觸自己的鹼基發生化學反應。這樣的系統天然就有高脫靶率的,可能之前大家對「沒有DNA鏈斷裂就沒有脫靶」形成了思維定勢,才會忽視這一安全漏洞。
長久以來,因為缺少令所有人都信服的脫靶檢測技術,基因編輯的脫靶問題被吵吵嚷嚷了五年多,也讓這個領域在此期間一直處於野蠻生長的狀態。

圖片來源:圖蟲創意
如今,GOTI出現了,規則還會遠嗎?(編輯:Yuki)
參考文獻:
Zuo, E.#, Sun, Y.#, Wu, W.#, Yuan, T.#, Ying, W., Sun, H., Yuan, L., Steinmetz, L., Li, Y.*, Yang, H.*(2019)Cytosine base editor generates substantial off-target single nucleotide variants in mouse embryos. Science Online
Schaefer, K. A., Wu, W. H., Colgan, D. F., Tsang, S. H., Bassuk, A. G., & Mahajan, V. B. (2017). Unexpected mutations after CRISPR-Cas9 editing in vivo. Nature methods, 14(6), 547-548.
|
|